Por Guilherme Oliveira Fevereiro 10, 2025
Resumo
Este trabalho tem como objetivo investigar formulações de otimização multiobjetivo para detecção de comunidades utilizando algoritmos evolutivos multiobjetivos para encontrar soluções eficientes.
Disponibilidade

O algoritmo Rapid Evolutionary Multi-objective Community Detection (re-mocd) está disponível como um projeto de código livre no GitHub, onde você pode escolher compilá-lo a partir do código-fonte ou usar a biblioteca pré-compilada a partir das releases. Ele também está disponível no PyPI do Python, permitindo instalação e uso de forma simples. Na data de publicação, a biblioteca possui 48 arquivos e 1.956 linhas de código. A biblioteca suporta dois modos de operação: via interface de linha de comando (CLI) ou por meio de chamadas diretas de funções utilizando a biblioteca PyPI.
Uso no PyPI
pip install re-mocd
Para a versão em Rust, será necessário construí-la a partir do código-fonte. As instruções para a construção podem ser encontradas no repositório oficial. A função run_rmocd pode ser chamada da seguinte forma:
import re_mocd
import networkx as nx
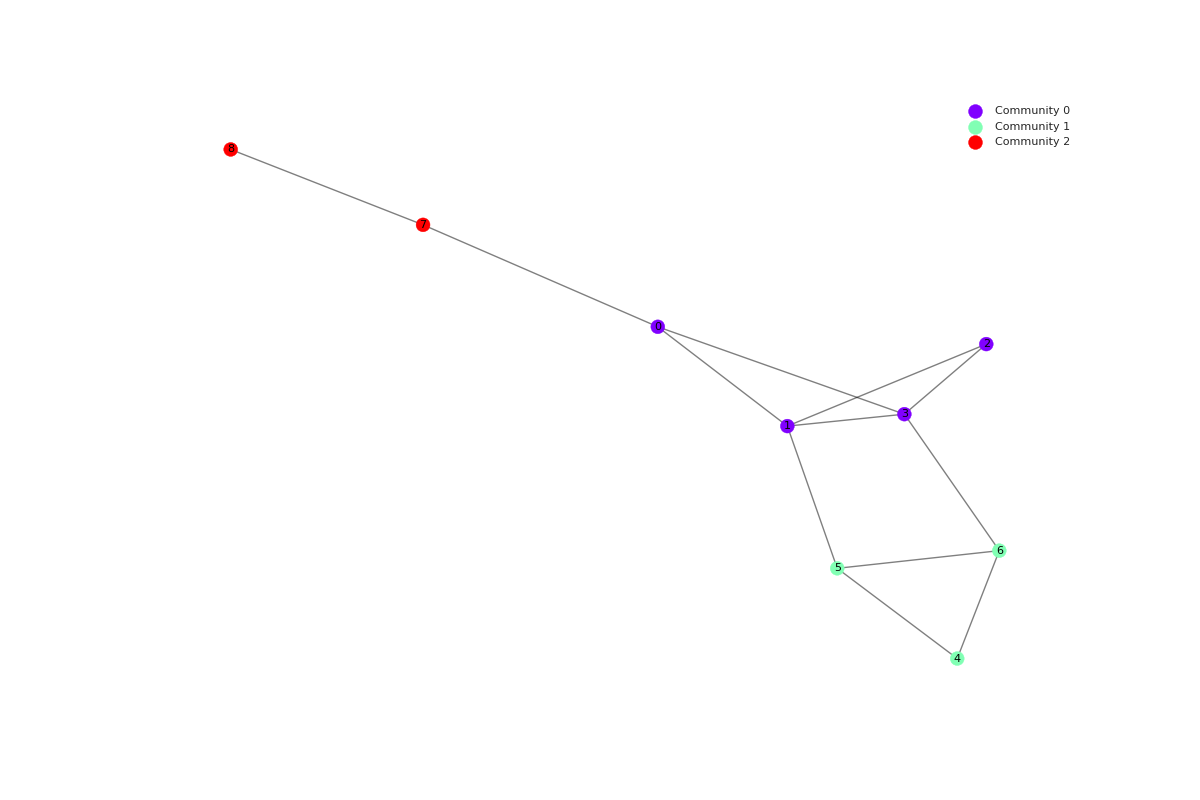
G nx.Graph([
(0, 1), (0, 3), (0, 7),
(1, 2), (1, 3), (1, 5),
(2, 3),
(3, 6),
(4, 5),
(4, 6),
(5, 6),
(7, 8)
])
partição = re_mocd.from_nx(G)
Dado o grafo acima definido pela biblioteca networkx, a função gerou a seguinte partição:
{0: 4, 1: 4, 2: 4, 3: 4, 4: 1, 5: 1, 6: 1, 7: 3, 8: 3}
Nesta representação, cada entrada corresponde a um par node:id, indicando a comunidade à qual cada nó pertence.
Modelo Matematico
Ao otimizar partições de grafos (ou detecção de comunidade), um objetivo comum é medir o quão “boa” é uma determinada partição. Em nossa implementação, calculamos duas métricas: uma que soma a comunidade interna ("intra") (ajustado para contagem dupla) e outra que usa os graus de nós pré-calculados para criar uma medida normalizada de conectividade entre uma comunidade e outras ("inter"), dada pela equaçao abaixo.
$$ Q(C) = \sum_{c \in C} \left[ \frac{|E(c)|}{m} - \left( \frac{\sum_{v \in c} \text{deg}(v)}{2m} \right)^2 \right], $$
Juntos, esses termos são combinados para produzir uma medida semelhante à modularidade (fixada entre –1 e 1). Mas o que isso significa em termos de desempenho? Vamos mergulhar nos detalhes.
Reorganizando a Partição em Comunidades
A primeira fase da nossa função reorganiza a partição—um mapeamento de cada nó para sua comunidade atribuída—em um hashmap que agrupa todos os nós por sua comunidade. Essa reorganização é direta: iteramos sobre cada nó na partição e adicionamos seu ID ao vetor correspondente.
- Tempo: Como processamos cada nó uma vez, esta etapa é $O(n)$, onde $n$ é o número de nós.
- Espaço: Um espaço extra de $O(n)$ é usado para armazenar esses grupos de comunidades.
Processando Cada Comunidade
Para cada comunidade, o algoritmo computa duas somas:
-
Arestas da Comunidade:
Para cada nó em uma comunidade, iteramos sobre seus vizinhos. O detalhe importante aqui é que precisamos contar apenas as arestas cujos dois extremos pertencem à mesma comunidade. Para isso, realizamos uma busca binária no vetor de nós da comunidade.-
Se um nó tem $d$ vizinhos e a comunidade tem $n₍c₎$ nós, cada busca binária custa $O(log n₍c₎)$.
-
Assim, para um nó, o custo é $O(d · log n₍c₎)$, e somando para todos os nós, o tempo total no pior caso será:
$ O(m \cdot \log n) $ onde $m$ é o número total de arestas no grafo.
-
-
Grau da Comunidade e Medida Normalizada:
Também recuperamos um grau precomputado para cada nó (de umhashmap, com custo médio $O(1)$ e atualizamos uma soma. Essa parte adiciona apenas uma sobrecarga constante por vizinho.
O tempo total para essa etapa é, portanto, dominado pela busca binária dentro da iteração dos vizinhos, resultando em um tempo de execução no pior caso de $O(m · log n)$.
Cálculo Final da Métrica
Depois que todas as comunidades são processadas (seja sequencialmente ou usando iteradores paralelos para melhorar o tempo de execução), a função calcula as métricas finais:
- Intra: Calculado como 1.0 menos a razão entre a soma das arestas intra‑comunidade e o número total de arestas.
- Modularidade: Computado como 1.0 menos a soma dos termos intra e inter, depois limitado ao intervalo [-1, 1].
Essa etapa envolve apenas algumas operações aritméticas, tornando-a essencialmente $O(1)$ em relação ao tamanho do grafo.
Complexidade Total
A complexidade total é a soma dos custos de construção das comunidades $O(n)$ e do processamento dos vizinhos $O(m · log n)$. Assim, a complexidade geral no pior caso é:
$ O(n + m \cdot \log n) $
Isso significa que, embora o algoritmo escale linearmente com o número de nós, o número de arestas (o fator mais pesado neste tipo de problema) é multiplicado por um fator logarítmico e continua eficiente para grafos esparsos.
Operadores Geneticos
Limitações dos Operadores Genéticos Tradicionais
Desafios do Crossover
A operação de crossover combina segmentos de duas soluções pais para produzir descendentes. Um método comumente utilizado, o crossover uniforme de dois pontos, é descrito da seguinte forma:
Escolhemos o crossover uniforme de dois pontos porque ele é imparcial em relação à ordem dos genes e pode gerar qualquer combinação de alelos a partir dos dois pais.
Embora seja versátil, essa abordagem é problemática para a detecção de comunidades devido aos seguintes motivos:
- Falta de percepção estrutural: Os pontos de crossover são escolhidos sem considerar a partição do grafo ou as propriedades estruturais.
- Degradação da qualidade: Os descendentes frequentemente não preservam as características das comunidades bem formadas, levando a soluções subótimas.
Desafios da Mutação
A mutação introduz pequenas mudanças aleatórias nas soluções para manter a diversidade genética. Na implementação tradicional1 explica:
Na operação de mutação, selecionamos aleatoriamente alguns genes e os atribuímos a outros nós adjacentes selecionados aleatoriamente.
No entanto, essa abordagem apresenta várias desvantagens:
- Mudanças cegas ao contexto: Ignora o contexto mais amplo da solução, frequentemente perturbando a integridade estrutural da partição.
- Ineficácia aleatória: As mutações podem levar a soluções mal construídas, particularmente quando nós críticos para a estrutura da comunidade são alterados de forma indiscriminada.
Desafios da Inicialização
A população inicial estabelece a base para o progresso evolutivo. descreve o processo tradicional de inicialização:
No processo de inicialização, geramos indivíduos aleatoriamente. Para cada indivíduo, cada gene $g_i$ escolhe aleatoriamente um dos nós adjacentes ao nó $i$.
Os principais problemas incluem:
- Pontos de partida de baixa qualidade: Partições aleatórias provavelmente não refletem estruturas de comunidade significativas.
- Ineficácia na busca: Começar muito longe de soluções promissoras dificulta a convergência no vasto espaço de busca.
Operadores Genéticos Otimizados
Crossover Inteligente
- Garantimos que o segundo ponto nunca esteja muito próximo do primeiro, limitando a extensão do crossover e prevenindo mudanças estruturais drásticas, além de preservar relações chave entre as comunidades, garantindo que as comunidades não sejam divididas ou mescladas arbitrariamente.
Mutação Inteligente
- Um cache de frequência é construído para analisar as comunidades dos vizinhos de um nó antes de decidir sua atribuição.
- Após construir o mapa de frequência das comunidades dos vizinhos de um nó, a função seleciona a comunidade mais frequente.
- Os nós para mutação são selecionados com base em uma taxa de mutação controlada (0,3), diferente da proposta de 0,6.
Referencias
-
Chuan Shi a, Zhenyu Yan, Yanan Cai, Bin Wu. Multi-objective community detection in complex networks. Elsevier, Beijing University of Posts and Telecommunications, Beijing Key Laboratory of Intelligent Telecommunications Software and Multimedia, Beijing 100876, China. Research Department, Fair Isaac Corporation (FICO), San Rafael, CA 94903, USA. Available at: https://www.sciencedirect.com/ ↩︎